Présentations
Voici une liste de présentations récemment données dans le cadre de séminaires et/ou workshops
-
8-Oct-2015 - Journées du GDR BIM, Institut Pasteur, Paris
The overall architecture of an RNA can be predicted with acceptable accuracy using established computational methods, such as those implemented in the MFold or the RNAFold software. This opens the door for a rational design of RNA molecules, to serve as building blocks in synthetic biology, or as novel therapeutic agents. To that purpose, one must solve the inverse folding problem, i.e. construct an RNA sequence which adopts a specific secondary structure according to established structure prediction methods. However, contrasting with the prediction task, the underlying computational structure of inverse folding is poorly understood, and existing tools either fail to return admissible sequences for some structures, or require extraordinary computational resources. Consequently, the field of RNA bioinformatics is currently craving for both practical and theoretically-sound approaches for the problem. In this talk, I will introduce the many flavors of the RNA design problem and illustrate its relevance to the objectives of modern (synthetic) biology. I will outline the strengths and shortcomings of selected approaches, and will briefly present recently contributed methods, developed with collaborators at Univ McGill (Canada), Wuhan Univ. (China) and Univ. Paris-Sud. If time allows, I will also mention results recently obtained with collaborators at Simon Fraser University, which characterize large subclasses of (un)designable secondary structures in simple energy models. These results are currently being extended to more realistic energy models, and could serve as a foundation for exact, computationally-efficient, solutions for RNA design. -
23-Jul-2015 - Benasque RNA meeting, Spain
Nous considérons une version minimaliste du Design d'ARN, la conception d'une séquence d'ARN se repliant de façon privilégiée dans une conformation d'intérêt. Ce problème est de complexité pour l'instant inconnue (il n'est même pas clair que le problème de décision associé soit dans NP). Nous décrivons des classes assez larges de structures admettant une solution pour le design, et etudions une généralisation du problème où la structure peut être modifiée de façon minimale. De façon assez surprenante, toutes les sous-classes caractérisées par nos travaux admettent des tests d'appartenance, ainsi que des procédures de conception de séquences, linéaires sur la taille des structures considérées, contrastant avec la complexité perçue (mais non-prouvée) du problème.
Travaux collaboratifs avec Jozef Hales (SFU, Canada), Jan Manuch (UBC/SFU, Canada) and Ladislav Stacho (SFU, Canada). -
6-Jun-2015 - CanaDAM'15@Saskatoon, Canada
Dans cet exposé, je résume la petite histoire de la bioinformatique de l'ARN, jalonnée par des interactions fructueuses entre biologistes, biochimistes, physiciens, mathématiciens et informaticiens. Au coeur de ces interactions, le concept de programmation dynamique, une technique algorithmique permettant la résolution efficaces de problèmes d'optimisation combinatoire en tirant parti d'une décomposition bien choisie pour l'espace de recherche. Des versions étendues et optimisées de cette technique permettent actuellement d'attaquer, à échelle génomique, des questions liées à l'analyse de l'ensemble de Boltzmann et à la relation séquence/structure/fonction chez les ARN. -
12-Jun-2014 - Cafés scientifique du consulat Français@Alliance Française Vancouver, Canada
Les ARN sont des biomolécules essentielles, qui n'en finissent pas de nous surprendre de par la diversité de leur mode d'action.Nous montrons comment la forme d'un ARN peut être prédite informatiquement (et efficacement !) à partir de sa séquence, grâce à un algorithme, une "recette de cuisine 2.0", qui ouvre la porte à de nombreuses applications biologiques et pharmaceutiques, et permet en passant d'éviter une émeute dans un village. -
10-Jun-2014 - Séminaire de maths discrète@SFU, Canada
Dans ce trvail commun avec Philippe Rinaudo, Alain Denise et Dominique Barth, nous utilisons le concept de la largeur arborescente pour unifier et prolonger un ensemble d'algorithmes proposés pour la comparaison structure/séquence dans les ARN. -
12-May-2014 - Cours@EPIT'14 - Ile d'Oléron, France
Les molécules d'ARN, naturellement encodées par des séquences sur l'alphabet {A,C,G,U}, se replient in vivo pour adopter une grande diversité de conformations, déterminant fortement leur fonction. Ce mécanisme du repliement est gouverné par l'appariement d'un ensemble de positions à travers la formation de liaisons hydrogènes. Il en découle une abstraction discrète de la conformation d'une molécule, la structure secondaire, qui peut être prédite en temps polynomial, et permet une représentation simplifiée, mais fidèle, de la structure d'ARN. Ce cours alternera deux interventions illustrant, dans le contexte du repliement d'ARN, l'utilisation des outils de la combinatoire énumérative et analytique pour la conception d'algorithmes de programmation dynamique.
Dans une première partie, nous présentons brièvement les notions de base sur l'ARN et nous décrivons quelques uns des principaux problèmes bioinformatiques et algorithmiques liés à l'analyse des séquences et des structures d'ARN. Nous nous attachons ensuite à décrire la représentation des séquences et structures d'ARN par des spécifications combinatoires. Nous focalisons une partie de l'exposé sur l'étude et la génération de séquences et structures aléatoires. Nous illustrons ainsi comment la combinatoire énumérative et la combinatoire analytique interviennent dans l'étude des propriétés des séquences, des structures, et des algorithmes qui les traitent.
Au sein d'une deuxième partie, nous expliquons comment ces spécifications peuvent être transformées, de façon générique, en des schémas récursifs sous-jacents à des algorithmes de programmation dynamique pour diverses applications. Parmi celles-ci, on pourra noter la prédiction de structure maximisant le nombre d'appariements, minimisant une notion d'énergie libre, ou bien permettant le calcul de la fonction de partition, une quantité essentielle en physique statistique. Nous montrons ensuite comment cette analogie peut être exploitée afin de dériver des familles d'algorithmes efficaces pour l'analyse, dans des séquences, de propriétés additives sur les séquences. Nous concluons avec une série de problème ouverts parmi lesquels le design d'ARN, i.e. la conception d'une séquence se repliant d'une façon prédéterminée et dont le statut au regard de la théorie de la complexité reste alors inconnu. -
15-Apr-2014 - PARC@SFU, Canada
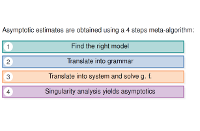
Au cours de cet exposé, nous rappelons les outils de base de l'analyse de singularité, et montrons comment ils peuvent être appliqués, dans le cadre d'un programme simple en quatre étapes inspiré de la méthode symbolique, pour étudier les propriétés asymptotiques des structures secondaires d'ARN. Cette méthodologie s'inscrit dans le cadre de la méthode symbolique, proposée par Flajolet et collaborateurs, et permet de nombreuses extensions, tel l'incorporation de pondérations, permettant d'induire des distributions de type Boltzmann. Nous illustrons ce cadre unificateur en dérivant diverses quantités, telle la distance moyenne entre les extrémités 5' et 3' d'un ARN, la distribution du nombre d'occurrences de motifs simples dans des conformations aléatoires d'ARN, la complexité moyenne d'algorithmes oeuvrant sur l'ARN, à travers la croissance asymptotique des RNA shapes, une représentation abstraite des structures d'ARN. Certains de ces résultats, en comparaison avec les données expérimentales, soulèvent des questions au sujet de la représentativité des modèles combinatoires "purs", proposés par analogie avec le modèle homopolymère de la physique statistique. -
17-Mar-2014 - ALEA'14@CIRM, Marseille
Survol, lors des journées ALEA'14, de résultats récents, obtenus en utilisant une approche génération aléatoire pour le design d'ARN. Travaux menés en collaboration avec de nombreux collaborateurs à UCSC (USA), Paris XI (France), Wuhan univ. (Chine), LIGM/Paris-Est (France), MIT (USA) et McGill (Canada). -
23-Sep-2013 - ACM-BCB'13@Washington, USA
Présentation d'une extension de notre méthode d'échantillonnage global pour le problème du design d'ARN sous contraintes. Travaux menés en collaboration avec Y. Zhou (UCSC, USA), A. Denise(LRI/IGM, Paris XI), Y. Zhang (Wuhan Univ., Chine), S. Vialette (LIGM, Paris-Est) et J. Waldispühl (McGill, Canada). -
15-Feb-2013 - Séminaire Vienna@Bled, Slovénie
Suite à une invitation au séminaire d'hiver de l'Institut de Biochimie Théorique (Vienna, à l'origine du Vienna Package) présentation d'un algorithme de complexité paramétrée basée sur une décomposition arborescente (Présenté à WABI'11), développé en collaboration avec P. Rinaudo, A. Denise et D. Barth (Slideshonteusement pompésadaptés de la soutenance de thèse de P. Rinaudo). -
28-Oct-2012 - Nuit des chercheurs, Polytechnique
L'équipe-projet Inria AMIB a animé le stand de l'Inria Saclay lors de la manifestation européenne de vulgarisation Nuit des chercheurs. J'ai conçu, en collaboration avec Laure Guion et Emmanuelle Perrot (Communication, Inria Saclay), une animation axée sur l'algorithmique du repliement et du design de l'ARN. J'ai en outre codé deux petits logiciels Java, l'un simulant le repliement [Jar] combinatoire de l'ARN, et l'autre explicitant le problème, nettement plus épineux, du design [Jar]. -
4-Jul-2012 - CPM'12@Helsinki, Finlande
En collaboration avec Rolf Backofen (Uni Freiburg, Allemagne) et Saad Sheikh (University of Florida, USA), nous résolvons quelques problèmes liés à la complexité du repliement des ARN avec pseudonoeuds généraux, dans des modèles d'énérgie d'expressivité croissante. Nous montrons que les modèles d'énergie basés sur les empilements de paires de bases rendent le repliement NP-difficile presque toujours, mais aussi toujours approximable, au moins dans un ratio 5. Par comparaison, nous montrons la complète inapproximabilité du problème pour au moins un modèle d'énérgie basé sur les plus proches voisins. -
18-Jun-2012 - AOFA'12@Montreal, Canada
Présentation de travaux communs avec Jérémie Du Boisberranger et Danièle Gardy (Prism, Université de Versailles St Quentin, France) sur une variante du collecteur de coupons. L'originalité de nos travaux est leur application aux langages pondérés, pour une large sous-classe desquels nous donnons un théorème général explicitant le temps d'attente de la collection complète. -
12-Jun-2012 - Retraite ARN/IGM@Seillac, France
Un bref exposé introductif, présenté en commun avec Alain Denise (LRI/IGM, Paris XI, France), décrivant les principales approches in silico disponibles pour la prédiction de structure des ARN. -
6-Apr-2012 - Unithé ou Café, INRIA Saclay, France
Un exposé de vulgarisation des principes sous-jacents à l'algorithmique du repliement des ARN. -
6-Mar-2012 - VIZBI'12, EMBL Heidelberg, Allemagne
Présentation générale des techniques et problématiques rencontrées dans la visualisation des ARN. -
5-Mar-2012 - VIZBI'12, EMBL Heidelberg, Allemagne
-
5-Sep-2011 - WABI'11, Saarbrücken, Allemagne
Présentation à WABI'11 (Saarbrücken, Allemagne) de travaux menés conjointement avec C. Saule (LRI/IRIC) utilisant des hypergraphes pour modéliser l'espace des repliements dans les algorithmes avec pseudo-noeuds. -
25-May-2011 - 12ème Salon Culture et Jeux Mathématiques, Paris
Co-animation du stand INRIA au 12ème salon Culture et Jeux Mathématiques (Paris). L'activité proposée tournait autour du thème du repliement de l'ARN, pour lequel nous proposions une activité manuelle ainsi qu'une présentation de vulgarisation scientifique (Voir l'application légère développée pour montrer les solutions). Activité proposée en collaboration avec M. Regnier, F. Lou, P. Rinaudo, V.-D. Tran, et A. Guilhot-Gaudeffroy (INRIA AMIB), ainsi qu'avec les services de communication des centres INRIA Saclay (L. Guion & E. Perrot) et Rocquencourt (A. Darnaud & H. Robak). -
25-Apr-2011 - IWBC/McGill@Barbados'11
Exposé au "1st Integrative Workshop on Biomolecular Complexes", présentant divers travaux utilisant des techniques de combinatoire discrète dans le contexte de la prédiction de structure et fonction de l'ARN. -
31-Mar-2011 - RECOMB'11@Vancouver, CA
Présentation d'un nouvel algorithme d'échantillonnage adaptatif pondéré permettant d'atteindre, à un surcoût minimal, des séquences issue d'une évolution sous contrainte. -
24-Feb-2011 - Sequence Processing'11@Dagstuhl
Formalisme d'hypergraphes et programmation dynamique pour le problème du repliement avec pseudonoeuds. Présentation d'extension naturelles vers des problèmes ensemblistes connexes. -
18-Mar-2011 - Séminaire MMC@Ecole PolytechniqueX
Présentation sur l'optimisation énergétique des ARN lors du séminaire Modélisation du métabolisme cellulaire organisé par Laurent Schwartz. -
14-Nov-2010 - Goupe de travail ROC, Strasbourg
Présentation des dernières extensions de VARNA en vue d'une intégration des recommandations du consortium Ontologie de l'ARN (ROC). -
3-Sep-2010 - Conférence GASCOM'10 (Montréal, Canada)
Présentation à l'UQAM (Montréal, Canada) lors de la conférence GASCOM'10 de travaux sur l'analyse de la redondance dans la génération pondérée, menés en collaboration avec Danièle Gardy (UVSQ). -
2-Sep-2010 - Computational Models for RNA à McGill (Montréal, Canada)
Exposé au centre de bioinformatique de l'université McGill (Montréal, Canada) au sein d'une série "Computational Models for RNA structures" décrivant des travaux récents sur l'extension d'une analogie hypergraphe pour la programmation dynamique sur les problèmes d'ARN. -
22-Mar-2010 - Séminaire du LACL (Paris XII/Créteil)
Une tentative de mise en évidence du lien unissant la combinatoire à l'évolution historique des algorithmes prédisant le repliement des ARN. -
22-Mar-2010 - Journées ALEA (Luminy)
Une réinterprétation combinatoire des principes du repliement in silico des ARN. -
25-Feb-2010 - Journées ARENA (Boussens)
Présentation des principes thermodynamiques et algorithmiques sous-jacents aux approches en moyenne pour le repliement de l'ARN à l'équilibre. -
25-Feb-2010 - Journées ARENA (Boussens)
Présentation des extensions récentes du logiciel VARNA dédié à la représentation des structures secondaires d'ARN : Sauvegarde de session, annotations de régions ... -
15-Dec-2009 - Séminaire OCAD (LIPN/Paris XIII)
Présentation de quelques résultats sur des problèmes d'énumération soulevés par l'étude du repliement de l'ARN. Plus spécifiquement, plaidoyer pour une étude combinatoire des espaces de conformations. -
27-Nov-2009 - Séminaire Bioinformatique (Université de Freiburg-Allemagne)
Courte présentation des méthodes génériques utilisées en combinatoire énumérative pour extraire des comportement asymptotique d'objets combinatoires simples (Langages rationnels et hors-contexte). Application à l'énumération des RNA shapes et discussion sur les limites d'une modélisation par des grammaires. -
20-Mar-2009 - Journées ALEA (Luminy)
Présentation préliminaire des principes et résultats de la génération aléatoire de Boltzmann multdimensionelle. Travail mené en collaboration avec O. Bodini (LIPN, Paris XIII) -
23-Jun-2008 - Conférence GASCOM'08 (Bibbiena-Italie)
Présentation d'un nouvel algorithme de génération aléatoire qui évite des objets déjà engendrés, tout en restant non biaisé (ex : Uniforme) parmi les objets restants.